本文主要是介绍生物信息学Bioinformatics学习笔记(四)- Data analysis-16sRNA,希望对大家解决编程问题提供一定的参考价值,需要的开发者们随着小编来一起学习吧!
Data analysis-16sRNA
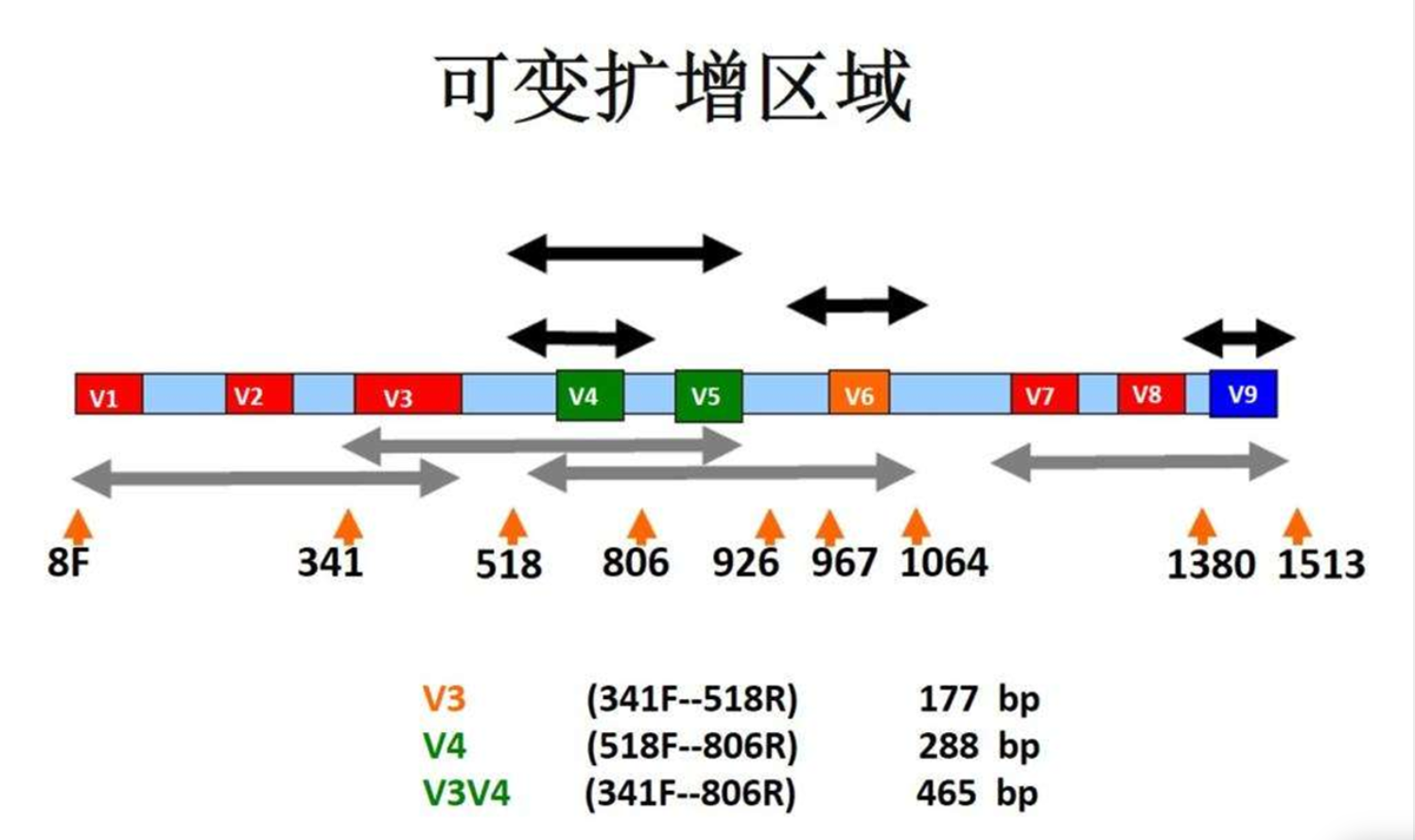
常用V3V4区域进行扩增子测序
Basic analytical procedure
1.原始数据处理
·去除接头序列,并将双端测序序列拼接成单条序列。
·根据测序barcode序列区分不同的样本序列。
·过滤低质量序列和无法比对到16s rDNA数据库的序列。
2.OTU(可执行操作单元)分类和统计
·以97%的序列相似度将所有序列进行同源比对并聚类成OTUs (QIIME -ucluster)
·与数据库GreenGenes比对 (uclust)http://greengenes.lbl.gov/cgi-bin/JD_Tutorial/nph-16S.cgi·对每个OTUs进行reads数目统计
3.样品构成丰度分析

随着测序量增加,逐渐达到平台期
4. Alpha多样性(样本内多样性)
[外链图片转存失败,源站可能有防盗链机制,建议将图片保存下来直接上传(img-qUpjIJ4r-1649297768484)(https://gitee.com/cling5899/Typora-img/raw/master/img/20220407085034.png)]
5.Beta多样性(样品间差异分析)
PCoA分析、NMDS分析、PCA分析
6.物种进化树的样本群落分布图
7.物种相关性分析
8.聚类分析
9.环境因子分析
这篇关于生物信息学Bioinformatics学习笔记(四)- Data analysis-16sRNA的文章就介绍到这儿,希望我们推荐的文章对编程师们有所帮助!