gwas专题
GWAS分析软件—— 一、Plink的安装
PLINK is a free, open-source whole genome association analysis toolset, designed to perform a range of basic, large-scale analyses in a computationally efficient manner. Plink是一个免费的,开源的全基因组关联分析的工具集,
scRNA+bulk+MR:动脉粥样硬化五个GEO数据集+GWAS,工作量十分到位
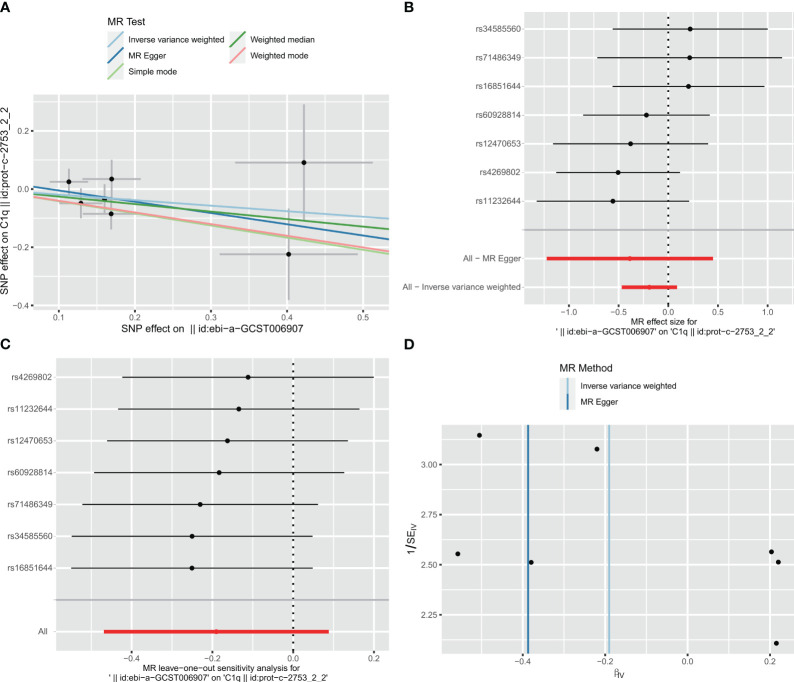
今天给大家分享一篇JCR一区,单细胞+bulk+MR的文章:An integrative analysis of single-cell and bulk transcriptome and bidirectional mendelian randomization analysis identified C1Q as a novel stimulated risk gene for Ather
成功案例|全基因组测序+GWAS联合分析揭示不同种族帕金森病的遗传同质性和异质性
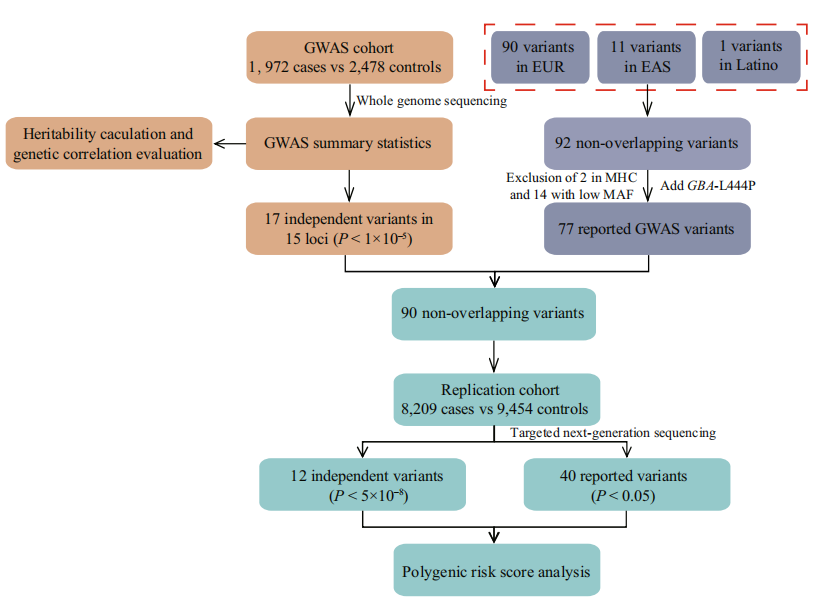
发表期刊:npj Parkinson’s Disease 影响因子:8.7 测序方式:WGS 研究对象:人 1 研究背景 帕金森病(PD)是一种常见的与年龄相关的神经退行性疾病,其特征是运动迟缓、姿势不稳定、僵硬和静息性震颤。临床表现包括非运动症状,如认知功能障碍、自主神经功能障碍、睡眠障碍、抑郁和睡眠功能减退。在中国,到2030年,PD患者的人数预计将达到494万人,占
【生信】QTL定位与全基因组关联分析(GWAS)
目录 遗传学知识 数量性状 分子标记(Molecular Marker) DNA分子标记的特点 QTL定位 QTL(quantitative trait locus) QTL定位的主要流程: 全基因组关联分析 GWAS(Genome-Wide Association Study,全基因组关联分析) GWAS的研究流程: 曼哈顿图和QQ-plot 知识补充 1.LOD值:
生信工具 | TIGA: Target Illumination GWAS Analytics
全基因组关联研究(GWAS)可以揭示重要的基因型-表型关联,但数据质量和可解释性问题必须得到解决。对于根据现有证据确定目标靶点的药物发现科学家来说,这些问题已不是单一的药物发现研究。作者开发的TIGA(Target Illumination GWAS Analytics)通过对全基因组关联研究(GWAS)中与性状相关的蛋白质编码基因进行评分和排序,促进药物靶点的发现。TIGA可以用相同的基因
GWAS power的计算
import mathimport numpy as npimport pandas as pdfrom matplotlib import pyplot as pltfrom scipy.special import chdtrifrom collections import defaultdict%matplotlib inline 对于GWAS中power值(statisti
GWAS软件:GEMMA的安装和使用教程
GCTA和GEMMA是GWAS分析中应用最广泛的两款软件,GCTA可以在Windows电脑下运行,而GEMMA软件只有Linux和Mac系统,这里介绍一下如何在Linux系统中安装GEMMA软件。 1. GEMMA名字来源 GEMMA名称来源: G: Genome-wide E:Efficient MM:Mixed-model A:Association 2. GEMMA下载地址
使用PLINK做GWAS(2)
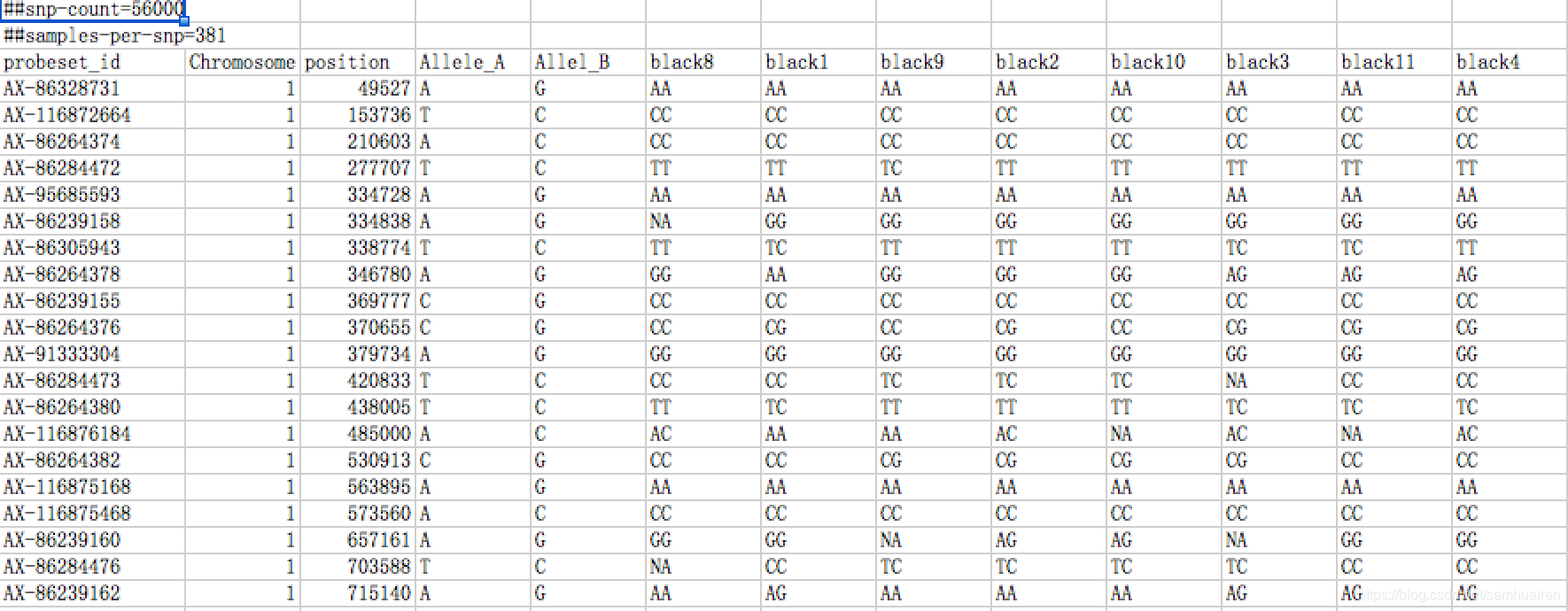
利用PLINK对单基因控制的性状进行定位,之前一篇文章粗滤的记录了一下使用PLINK的命令,本次博客主要记录一下如何根据SNP芯片的数据制作PLINK的格式,以及分析的步骤,最后数据的可视化。 首先,有的公司给的新片的数据就是一个excel表格,列表示的是样品,行表示的是基因型,基因型用ATCG构成,当然有的基因型是用数字0或者1表示的。下面我拿到的一个数据是15个样品构成的基因型,有13个样品
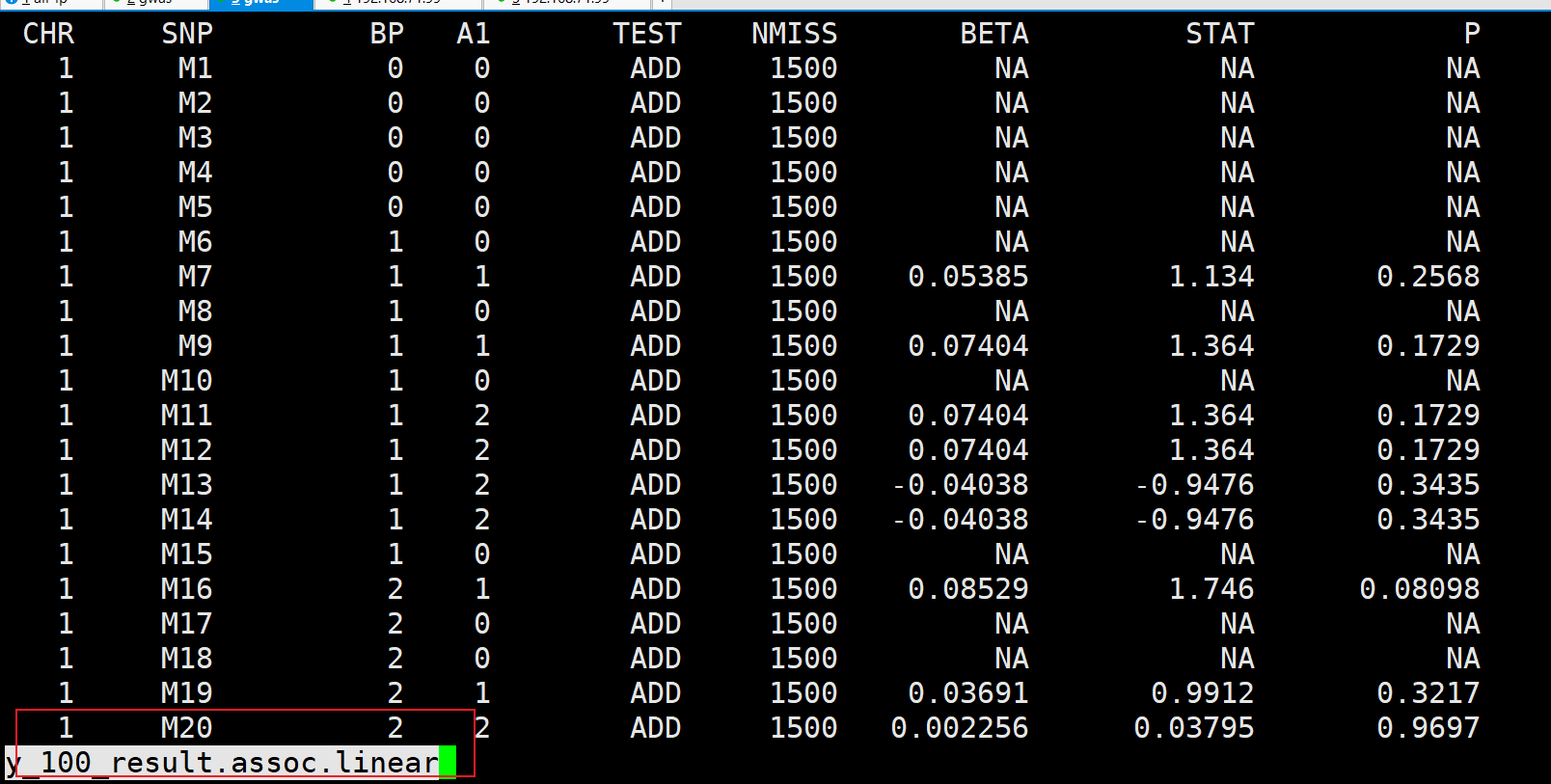
plink分析100个性状的批量gwas分析
大家好,我是邓飞。 GWAS分析时,3~5个性状是正常操作,要分析100个性状呢,手动修改参数,工作量是够了,但是程序员的修养体现在哪里了??? 如果还是按照每个性状一个文件夹,每个文件夹中一个脚本,不断地修改脚本,一点也不高端,所以,遇到这种情况,批量处理就派上用场了。 之所以之前一直不用,因为10个性状一下,没有必要,费心思想还不如直接动手操作了,但是100个性状真的吓到我了,不满足才能